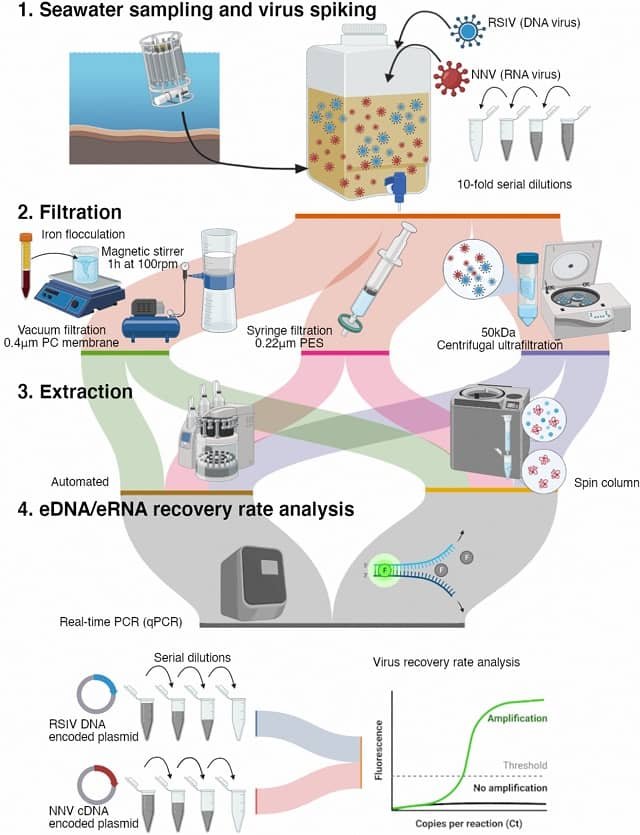
El monitoreo de la biodiversidad en ecosistemas acuáticos ha experimentado una metamorfosis gracias al ADN ambiental (eDNA). Esta técnica permite identificar qué especies habitan un cuerpo de agua al analizar las trazas genéticas que dejan a su paso. Sin embargo, la precisión de esta «huella digital» biológica se ha visto obstaculizada por bases de datos incompletas, secuencias contaminadas y especies que, a nivel genético, parecen gemelas.
Para resolver estos cuellos de botella, un equipo de investigadores liderado por Tao Zhu y Susumu Yoshizawa de The University of Tokyo ha lanzado MitoNGS, una plataforma web de nueva generación que sustituye a la exitosa MiFish. Este sistema no solo amplía la capacidad de análisis, sino que también introduce una inteligencia contextual sin precedentes en la bioinformática marina.
- 1 Conclusiones clave del estudio
- 2 Diferencias Clave: ¿Por qué MitoNGS supera a MiFish?
- 3 Estrategias para una Identificación Taxonómica de Alta Precisión
- 4 Impacto Global y Resultados: Desde Japón hasta la Amazonía
- 5 Desafíos y Perspectivas Futuras en la Biomonitorización Genómica
- 6 Relevancia Estratégica en la Gestión de Recursos Acuícolas
- 7 Conclusión: El Nuevo Estándar en la Biomonitorización Global
- 8 Entradas relacionadas:
Conclusiones clave del estudio
- Compatibilidad total: MitoNGS analiza datos de cualquier marcador mitocondrial (12S, 16S, COXI, CYTB) y plataformas de secuenciación como Illumina y Nanopore.
- Resolución mediante «especies complejas»: Introduce una estrategia para gestionar taxones con secuencias idénticas, utilizando datos de hábitat y de distribución geográfica para filtrar los resultados.
- Limpieza de datos contaminados: Identifica y excluye regiones «heterospecíficas» (mislabeled) de las bases de datos de referencia para evitar falsos positivos.
- Eficiencia en tiempo real: Es significativamente más rápida que otras herramientas, procesando bibliotecas complejas de Nanopore en minutos.
- Interfaz accesible: Ofrece una solución web gratuita y fácil de usar para investigadores y gestores de recursos biológicos.
Diferencias Clave: ¿Por qué MitoNGS supera a MiFish?
La superioridad de MitoNGS radica en su avanzado motor de procesamiento y la solidez de su base de datos de referencia, MitoFish. Mientras que el pipeline original de MiFish se limita a cebadores universales de 12S rRNA, MitoNGS es una plataforma integral que admite diversos loci mitocondriales. Esta versatilidad es crucial para la industria biotecnológica, ya que permite emplear marcadores como COXI o CYTB según los requerimientos específicos de cada investigación.
Validación de Regiones Heterospecíficas
Un desafío crítico en GenBank es la proliferación de secuencias quiméricas: fragmentos de ADN donde coexisten la especie objetivo y contaminantes. Para mitigar esto, MitoNGS fragmenta los genes mitocondriales en segmentos de 100 pb y los valida frente a homólogos de diversos autores. Si una región coincide únicamente con especies distintas, se clasifica como heterospecífica y se excluye del análisis para garantizar la integridad de los resultados.
El Enfoque de «Complejo de Especies»
Cuando dos especies presentan un marcador de metabarcoding idéntico (100% de identidad), los sistemas convencionales suelen fallar. MitoNGS resuelve esto agrupando a estos taxones en un especies complex. Para una resolución precisa, el sistema cruza la información con variables externas:
- Parámetros de hábitat: Salinidad, profundidad y zona climática (mediante rFishBase).
- Distribución geográfica: Registros de ocurrencia global (vía GBIF).
Optimización para Secuenciación de Tercera Generación (Nanopore)
A diferencia de su predecesor, MitoNGS está optimizado para las lecturas largas y complejas de plataformas como Nanopore. Utiliza el algoritmo VSEARCH para generar variantes de secuencia de amplicones (ASVs) de alta fidelidad a partir de datos crudos. Esto facilita el monitoreo ambiental en tiempo real mediante dispositivos portátiles como el MinION.
Estrategias para una Identificación Taxonómica de Alta Precisión
Uno de los desafíos más críticos del metabarcoding es la ambigüedad secuencial, fenómeno que ocurre cuando una secuencia de ADN presenta una coincidencia del 100% con múltiples especies. Para mitigar este obstáculo, MitoNGS implementa protocolos avanzados de discriminación:
Validación Taxonómica de Subregiones
El sistema descompone las secuencias en fragmentos de 100 pb (pares de bases) para identificar con rigor contaminaciones cruzadas o errores de etiquetado preexistentes en GenBank. Este proceso permite detectar regiones heterospecíficas, garantizando que la asignación taxonómica no se vea comprometida por secuencias mal curadas en bases de datos públicas.
Integración de Metadatos Ambientales y Geográficos
La plataforma trasciende la bioinformática pura al integrar variables ecológicas de rFishBase (profundidad, salinidad y zona climática) y registros de ocurrencia global de GBIF.
Mantente siempre informado
Únete a nuestras comunidades para recibir al instante las noticias, informes y análisis más importantes del sector acuícola.
En escenarios donde dos especies comparten una identidad genómica idéntica, el sistema permite discernir la taxonomía correcta mediante el cruce de datos biogeográficos. Por ejemplo, si una especie habita en ecosistemas árticos y la otra en regiones tropicales, el software prioriza la asignación según las coordenadas geográficas de la muestra recolectada.
Impacto Global y Resultados: Desde Japón hasta la Amazonía
La eficacia de la plataforma MitoNGS ha sido validada mediante ocho conjuntos de datos heterogéneos, que abarcan desde el río Uchidomari en Japón hasta la Amazonía peruana y diversos sistemas de acuarios en los Países Bajos. Esta diversidad geográfica subraya la versatilidad del sistema en distintos ecosistemas acuáticos.
Rendimiento y Precisión Analítica
En fases de prueba, MitoNGS demostró una superioridad técnica significativa frente a soluciones competidoras. Durante el análisis de una librería de Nanopore con lecturas de 2 kb, el sistema completó el procesamiento en solo 8 minutos, contrastando drásticamente con las más de 2 horas requeridas por el pipeline DECONA.
Asimismo, la plataforma logró identificar 15 especies adicionales que habían pasado desapercibidas en los estudios originales. Este incremento en la sensibilidad taxonómica se debe a la robusta cobertura de su base de datos, la cual se mantiene en constante actualización.
Resolución de Conflictos Genéticos
MitoNGS ha demostrado una capacidad superior para resolver ambigüedades taxonómicas. El sistema permitió asignar identidades específicas a especímenes que originalmente fueron reportados como «clados generales».
Un caso destacado es la identificación precisa de Caracanthus unipinna en la Isla Europa. Este nivel de resolución es posible gracias a que la base de datos MitoFish se actualiza mensualmente, garantizando que los investigadores trabajen siempre con la información genómica más reciente disponible.
Desafíos y Perspectivas Futuras en la Biomonitorización Genómica
A pesar de su sofisticación tecnológica, MitoNGS reconoce y aborda los retos intrínsecos al estado actual de la genómica ambiental. Estas limitaciones definen la hoja de ruta para futuras innovaciones:
- Brechas en las secuencias de referencia: Persisten vacíos críticos en familias de peces poco comunes, como Scytalinidae o Lacantuniidae, para las cuales aún no existen secuencias mitocondriales disponibles en las bases de datos globales.
- Complejidad por Hibridación: La presencia de híbridos naturales en ciertos complejos de especies puede desdibujar las fronteras genéticas. Este fenómeno representa un desafío para la resolución taxonómica de marcadores específicos donde la diferenciación es mínima.
- Interferencia por ADN Bacteriano: En el uso de marcadores como COXI, el sistema puede detectar secuencias de origen bacteriano. Para mitigar esta señal de fondo, se requiere una expansión continua de las bases de datos de referencia que permita filtrar con mayor precisión el material no objetivo.
Relevancia Estratégica en la Gestión de Recursos Acuícolas
MitoNGS trasciende la definición de un simple software para consolidarse como un ecosistema de datos integrados. Al permitir la carga de ASVs/OTUs propios para reanálisis dinámicos, la plataforma impulsa una ciencia más colaborativa, transparente y reproducible.
Para los profesionales del sector, la herramienta optimiza la gestión de múltiples muestras, integrando de forma nativa:
- Controles y Réplicas: Manejo visual de controles positivos, negativos y réplicas biológicas.
- Mitigación de Errores: Identificación proactiva de contaminaciones cruzadas en laboratorio, reduciendo drásticamente el riesgo de falsos positivos.
- Resultados Auditables: Presentación de datos en tablas analíticas que facilitan la toma de decisiones críticas.
Esta robustez técnica asegura que los informes sobre especies invasoras o el estado de salud de los stocks pesqueros sean plenamente fiables y cumplan con los más altos estándares de auditoría científica.
Conclusión: El Nuevo Estándar en la Biomonitorización Global
MitoNGS se consolida como el estándar de oro para el análisis de metabarcoding de peces, logrando una sinergia inédita entre velocidad, precisión y una interfaz web diseñada para la democratización de la genómica. Al resolver con éxito el desafío de las secuencias ambiguas y optimizar la compatibilidad con tecnologías de vanguardia como Nanopore, la plataforma garantiza un monitoreo más robusto y fiable de la biodiversidad acuática global.
Este ecosistema rompe las barreras tradicionales del sector: hoy, cualquier investigador con una computadora portátil y conexión a internet puede ejecutar análisis de alta complejidad. Lo que antes demandaba el uso de supercomputadoras y expertos en bioinformática de línea de comandos, ahora es accesible para la comunidad científica global, facilitando una gestión ambiental más ágil y basada en datos.
Esta investigación fue apoyada por: Ocean DNA Project (No. 027) from Future Society Initiative, Interdisciplinary Collaborative Research Program (1-B) of Atmosphere and Ocean Research Institute, the University of Tokyo, y MEXT Advancement of Technologies for Utilizing Big Data of Marine Life JPMXD 1521474594.
Contacto
Tao Zhu
Department of Integrated Biosciences, Graduate School of Frontier Sciences, The University of Tokyo.
Department of Natural Environmental Studies, Graduate School of Frontier Sciences, The University of Tokyo.
Correo: zhutao@edu.k.u-tokyo.ac.jp
Susumu Yoshizawa
Department of Natural Environmental Studies, Graduate School of Frontier Sciences, The University of Tokyo.
Atmosphere and Ocean Research Institute, The University of Tokyo.
Correo: yoshizawa@aori.u-tokyo.ac.jp
Referencia (acceso abierto)
Zhu, T., Sato, Y., Fukunaga, T., Miya, M., Iwasaki, W., & Yoshizawa, S. (2026). MitoNGS: an online platform to analyze fish metabarcoding data in high resolution. Molecular Biology and Evolution, 43(3), 1-15. https://doi.org/10.1093/molbev/msag046
Editor de la revista digital AquaHoy. Biólogo Acuicultor titulado por la Universidad Nacional del Santa (UNS) y Máster en Gestión de la Ciencia y la Innovación por la Universidad Politécnica de Valencia, con diplomados en Innovación Empresarial y Gestión de la Innovación. Posee amplia experiencia en el sector acuícola y pesquero, habiendo liderado la Unidad de Innovación en Pesca del Programa Nacional de Innovación en Pesca y Acuicultura (PNIPA). Ha sido consultor senior en vigilancia tecnológica, formulador y asesor de proyectos de innovación, y docente en la UNS. Es miembro del Colegio de Biólogos del Perú y ha sido reconocido por la World Aquaculture Society (WAS) en 2016 por su aporte a la acuicultura.